ARTIGOS ORIGINAIS
ESTUDO COMPARATIVO DE MODELOS COMPUTACIONAIS GERADOS SOBRE REPRESENTAÇÕES DE IMAGENS DE COLOSCOPIA: TECIDO DE MUCOSA NORMAL VS TECIDO DE MUCOSA DE PÓLIPO CÓLICO
Comparative Study of Computacional Models Generated from Representations of Colonoscopic Images: Normal Mucosal Tissues VS Mucosal Tissues of Colic Polyp
CARLOS ANDRES FERRERO1, HUEI DIANA LEE2, NEWTON SPOLAÔR3, CLÁUDIO SADDY RODRIGUES COY4, JOÃO JOSÉ FAGUNDES5, RENATO BOBSIN MACHADO6, EVERTON ALVARES CHERMAN3, FENG CHUNG WU7
1Pesquisador do Laboratório de Bioinformática (LABI), Universidade Estadual do Oeste do Paraná (UNIOESTE), Parque Tecnológico Itaipu (PTI), Foz do Iguaçu, PR, Brasil; 2 Professora Doutora e Coordenadora do Curso de Ciência da Computação da UNIOESTE e Coordenadora Geral do LABI - UNIOESTE, Foz do Iguaçu, PR, Brasil; 3 Estagiário do Laboratório de Bioinformática (LABI), Universidade Estadual do Oeste do Paraná (UNIOESTE), Parque Tecnológico Itaipu (PTI), Foz do Iguaçu, PR, Brasil; 4 Professor Doutor do Departamento de Cirurgia (D.M.A.D.), Serviço de Coloproctologia da Universidade Estadual de Campinas (UNICAMP), Campinas, SP, Brasil; 5 Professor Doutor do Departamento de Cirurgia da Faculdade de Ciências Médicas da UNICAMP, Campinas, SP, Brasil; 6 Professor e Coordenador da Área Computacional do LABI - UNIOESTE, Foz do Iguaçu, PR, Brasil; 7 Pesquisador do Serviço de Coloproctologia da Faculdade de Ciências Médicas da UNICAMP, Campinas, SP, Brasil. Professor Doutor da UNIOESTE e Coordenador da Área Médica do LABI - UNIOESTE, Foz do Iguaçu, PR, Brasil.
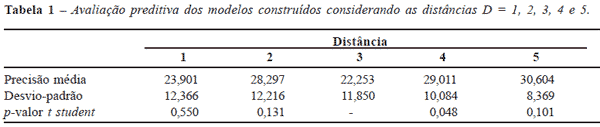
Resumo: Objetivo: analisar a qualidade preditiva de modelos computacionais para a diferenciação de tecidos cólicos, construídos a partir da representação de Imagens de Coloscopia (IC) como Matrizes de Co-ocorrência (MC). Materiais e Métodos: os modelos foram construídos aplicando técnicas de análise de imagens e de inteligência artificial. Foram utilizadas 67 IC, contendo pólipos, a partir das quais foram extraídas uma imagem da parte de tecido de pólipo e outra de tecido sem pólipo adjacente, totalizando 134 imagens. Para cada imagem, foram construídas MC para diferentes valores do parâmetro distância, D = 1 a 5, e extraídas 11 características de textura. Com essa representação, foram criados cinco modelos computacionais baseados em árvores de decisão. Os modelos foram avaliados utilizando: (a) validação cruzada e (b) tabelas de contingência. Resultados: na análise (a), o modelo de D = 3 apresentou o menor erro médio (22,25% ± 11,85%). Na análise (b), os modelos de D = 1 e 3 apresentaram os melhores valores de precisão. Conclusão: os valores do parâmetro de distância D = 1 e 3 apresentaram os modelos com as melhores qualidades preditivas. Os resultados mostraram que os modelos construídos apresentaram-se promissores para a construção de sistemas computacionais de suporte à decisão.
Descritores: Colonoscopia, Polipose Intestinal, Neoplasias do Cólon, Inteligęncia Artificial, Interpretaçăo de Imagem Assistida por Computador.
INTRODUÇÃO
Exames médicos são registrados,
frequentemente, em hospitais e clínicas médicas, por meio
da utilização de Sistemas de Gerenciamento de Dados,
os quais possibilitam que registros com informações
de pacientes e de exames relacionados, sejam
armazenados e consultados pelos especialistas. A descrição
desses exames pode estar representada em diversos
formatos, como texto, imagem e
vídeo(1,2), com o objetivo de complementar os laudos médicos realizados
pelos especialistas e, desse modo, prover uma descrição
mais completa a respeito do estado de saúde do paciente.
Nesse sentido, imagens médicas
provenientes de exames coloscópicos, por exemplo, têm
sido comumente armazenadas com o intuito de prover
esse complemento e dar suporte aos especialistas no
diagnóstico de enfermidades. Ainda, essas imagens,
podem ser analisadas por processos computacionais que
permitam extrair informações relevantes a respeito
das anormalidades evidenciadas por meio desse
exame. Duas áreas para prover suporte a essa tarefa são:
(1) Análise de Imagens e (2) Inteligência
Computacional. A primeira refere-se à extração de informações
relevantes em imagens e, a segunda, à busca de padrões
e à construção de
modelos(3), os quais permitem classificar imagens nunca antes classificadas.
No Brasil, segundo o Instituto Nacional do Câncer (INCA), o câncer colorretal constitui uma
das neoplasias malignas de maior incidência na
população, ocupando o quarto lugar em relação ao sexo
masculino e o terceiro lugar em relação ao sexo
feminino(4). De acordo com o INCA, no ano de 2008, haverá
aproximadamente 12.490 casos desse tipo de câncer em
homens e 14.500 em mulheres. Em relação à
mortalidade média mundial, o câncer de cólon e reto, não
apresenta grandes diferenças entre países desenvolvidos
e países em desenvolvimento(4). A coloscopia
apresenta-se como uma ferramenta indispensável para o
diagnóstico de doenças do intestino grosso, o que
torna importante a análise computacional para a
identificação automática de anormalidades evidenciadas por
esse exame médico.
O presente trabalho está inserido em um
projeto maior, de Análise de Imagens Médicas, o qual
é desenvolvido em uma parceria entre o LABI/UNIOESTE e o SC/FCM/UNICAMP. Nesse
contexto, este trabalho tem como objetivo analisar a
qualidade preditiva de modelos computacionais para a
diferenciação de tecidos cólicos, construídos a partir
da representação de Imagens de Coloscopia (IC)
como Matrizes de Co-ocorrência (MC).
MATERIAIS E MÉTODOS
Para a realização deste trabalho, 67
imagens de exames de coloscopia, provenientes do
SC/FCM/UNICAMP, referentes a pólipos do tipo
Protruso Pediculado (de acordo com os padrões da
Sociedade Japonesa do Câncer Colorretal), foram submetidas
a uma metodologia que possibilita a extração de
características intrínsecas de fragmentos de imagem de
tecido cólico e a busca de padrões para a construção
de modelos de
classificação(5). Essa metodologia, a qual
é apoiada por um sistema computacional
desenvolvido no LABI/UNIOESTE, denominado Medical
Image Analysis System (MIAS)(5,6), é constituída de
quatro etapas: (1) coleta do Conjunto de Imagens (CI);
(2) construção do Vetor de Características (VC); (3)
construção de modelos de classificação; e (4) avaliação
de modelos.
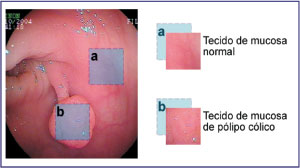
Na Etapa (1) foi realizada a coleta do conjunto de imagens para análise. Para cada imagem
foram selecionadas uma parte de imagem de mucosa
normal e outra de pólipo cólico (Figura 1). Desse modo,
foi construído o CI contendo 134 imagens, cada uma
referente a uma das partes selecionadas. Na Etapa
(2) essas imagens foram submetidas ao processo de
extração de características. Neste trabalho foram
extraídas características de textura, baseadas em MC,
as quais representam as transições de nível de
intensidade entre pontos da imagem considerando uma
distância e uma
direção(2).
 |
Figura 1 - Seleção de fragmentos de tecido de mucosa normal e
de pólipo cólico. |
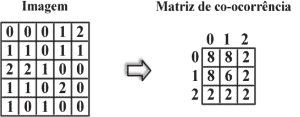 |
Figura 2 - Imagem representada em três níveis de cinza
como uma matriz de pixels 5x5 e a respectiva MC para a direção 0º e
a distância 1. |
 |
 |
 |
 |
 |
 |
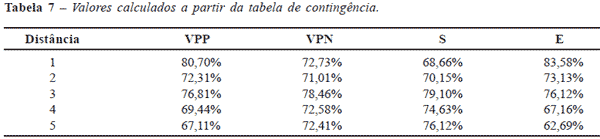 |
ABSTRACT: Purpose: to evaluate the predictive quality of computational models to differentiate colic tissues, based on Co-occorrurence Matrices (MC) representation of Coloscopic Images (IC). Materials and Methods: image analysis and artificial intelligence methods were employed to construct computational models. Sixty seven IC images, containing polyp, were considered in this work, from which a part containing a polypus and another without it were collected given origin to 134 images. For each one of these, different MC were constructed considering five distance parameters (D = 1 to 5) and the extraction of 11 texture characteristics. With this representation, five computational models were generated based on decision trees. These models were evaluated using two techniques: (a) cross-validation and (b) contingency tables. Results: for the (a) analysis, the model with D = 3 presented the smaller average error (22.25% ± 11.85%). For the (b) analysis, models with D = 1 and 3 presented the best precision values. Conclusion: parameters D = 1 and 3 presented models with the best predictive qualities. Results showed that the constructed models were promising to be applied within decision making computational systems.
Key words: Colonoscopy, Intestinal Polyposis, Colonic Neoplasms, Artificial Intelligence, Image Interpretation.
Referências
1. Karkanis S, Galoussi K, Maroulis D. Classification
of Endoscopic Images Based on Texture Spectrum.
Advance Course in Artificial Intelligence. Proceedings of Workshop
on Machine Learning in Medical Applications; 1999;
Chania, Grecia; p. 63-7.
2. Felipe JC, Traina AJM, Traina C. Retrieval by Content
of Medical Images Using Texture for Tissue
Identification. Proceeding of the 16th IEEE Symposium on
Computer-based Medical Systems; 2003; New York, USA; p 175-6.
3. Rezende SO. Sistemas Inteligentes: Fundamentos e
Aplicações. Barueri (SP), Brasil: Editora Manole; 2003.
4. Instituto Nacional de Câncer (INCA). Estimativa 2008:
Incidência de Câncer no Brasil. Rio de Janeiro (RJ), Brasil; 2007.
5. Ferrero CA, Lee HD, Cherman E A, Coy CSR, Fagundes
JJ, Góes JRN, et al. Utilização de Atributos Baseados em
Textura para a Caracterização de Tecidos Cólicos em Imagens
de Colonoscopia. Anais do VII Workshop de Informática
Médica. 2007; Porto de Galinhas (PE), Brasil; p. 204_213.
6. Ferrero CA, Spolaôr N, Lee HD, Coy CSR, Fagundes JJ,
Wu FC. Estudo Comparativo de Matrizes de Co-ocorrência
em Análise de Imagens Médicas: Diferenciação de Tecidos
Cólicos. Anales del 11º Simposio Argentino de Informática y Salud,
37º Jornadas Argentinas de Informática; 2008; Santa Fe (SF),
Argentina; p. 1_12.
7. Haralick R; Shanmugam K; Dinstein I. Texture Features
for Image Classification. Proceeding of IEEE Transaction
on Systems, Man, and Cybernetis. 1973; 3(6): p. 610_621.
8. Quinlan JR. C4.5: Programs for Machine Learning. San
Mateo (CA), USA: Editora Morgan Kaufmann; 1993.
9. Doria U. Introdução à Bioestatística: para simples
mortais. São Paulo (SP), Brasil: Editora Elseiver; 1999.
10. Howarth P, Yavlinsky A, Heesch D, Rüger S. Medical
Image Retrieval Using Texture, Locality and Colour. Lecture
Notes from the Cross Language Evaluation Forum. 2005; p.
740-749.
11. Karkanis S, et al. Detecting Abnormalities in
Colonoscopic Images by Textural Description and Neural
Networks. Proceedings of Workshop on Machine Learning in
Medical Applications, Advance Course in Artificial Intelligence;
1999; Chania, Greece; p. 5:59-62.
12. Ferrero CA, Lee HD, Cherman EA, Coy CSR, Góes
JRN, Fagundes JJ, Wu FC. Utilização de Técnicas
Computacionais para a Diferenciação Cólicos em Imagens Colonoscópicas.
56º Congresso Brasileiro de Coloproctologia: Rev Bras
de Coloproct 2007; Curitiba (PR), Brasil; 27: p. 45_46.
1 http://www.cs.waikato.ac.nz/ml/weka/.
2 http://www.graphpad.com/.
Endereço para correspondência:
Carlos Andres Ferrero
Laboratório de Bioinformática (LABI)
Universidade Estadual do Oeste do Paraná (UNIOESTE)
Parque Tecnológico Itaipu (PTI)
Av. Tancredo Neves, 6731
CEP: 85.856-970 / Caixa Postal: 39
Foz do Iguaçu _ Paraná _ Brasil
Fax: (45) 3522-3462
E-mail: anfer86@gmail.com
Recebido em 25/10/2008
Aceito para publicação em 13/11/2008
Trabalho realizado no Laboratório de Bioinformática (LABI), Universidade Estadual do Oeste do Paraná (UNIOESTE), Parque
Tecnológico Itaipu (PTI), e no Serviço de Coloproctologia (SC) da Faculdade de Ciências Médicas (FCM) da Universidade Estadual de
Campinas (UNICAMP).
Conflito de Interesses: nenhum
Fonte de auxílio à pesquisa: Programa de Desenvolvimento Tecnológico Avançado - Fundação Parque Tecnológico Itaipu
(PDTA/FPTI-BR). Termos de Concessão de Bolsa 009/2007, 041/2008 e 087/2008. Fundação de Apoio ao Desenvolvimento Científico e Tecnológico do
Paraná (ARAUCARIA). Convênio 051/2007.